2024年2月23日,来自华中科技大学黄胜友等研究人员合作在学术期刊《自然—生物技术》上发表了标题为“All-atom RNA structure determination from cryo-EM maps.”的研究成果,实现根据冷冻电镜图谱确定全原子RNA结构。
研究人员表示,从冷冻电镜图谱中确定蛋白质结构的方法很多,但对于RNA结构来说,这仍然是一项挑战。
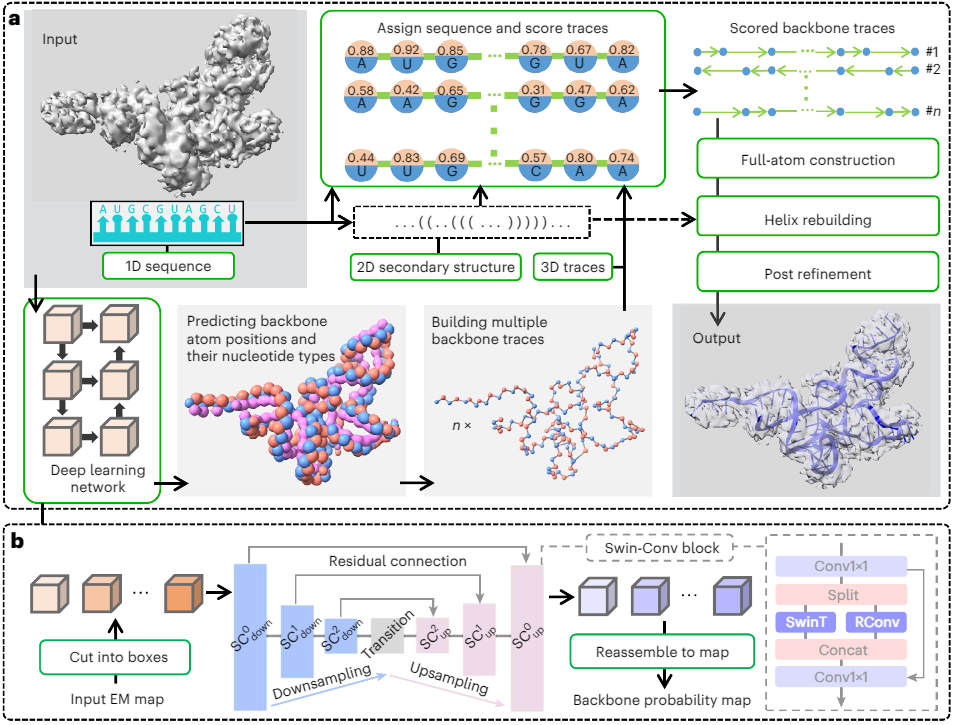
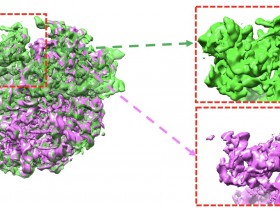
研究人员开发了EMRNA,这是一种从冷冻电镜图谱中准确、自动确定全长全原子RNA结构的方法。EMRNA整合了基于深度学习的核苷酸检测、三维骨架追踪、考虑序列和二级结构信息的评分以及RNA结构的全原子构建。研究人员在分辨率为2.0-6.0 Å、长度从37nt到423nt的140个不同RNA图谱上验证了EMRNA,并在一组71个案例中将EMRNA与auto-DRRAFTER、phenix.map_to_model和CryoREAD进行了比较。
对于全长RNA结构,EMRNA的中位精确度为2.36 Å均方根偏差和0.86 TM-score,而auto-DRRAFTER为6.66 Å和0.58。在构建的模型中,EMRNA还获得了较高的残基覆盖率和序列匹配率,分别为93.30%和95.30%,而phenix.map_too_model为58.20%和42.20%,CryoREAD为56.45%和52.3%。EMRNA的速度很快,能在3分钟内构建100 nt的RNA结构。
文章来源:
Li, Tao, He, Jiahua, Cao, Hong et al, All-atom RNA structure determination from cryo-EM maps.DOI: 10.1038/s41587-024-02149-8,Nature Biotechnology:最新IF:68.164